Next: 24 Intervalos de confiança Up: Curso sobre o programa Previous: 22 Ilustrando propriedades de
A função de verossimilhança é central na inferência estatística. Nesta sessão vamos ver como traçar funções de verossimilhança utilizando o programa R.
Seja o vetor
![]() uma amostra aleatória de uma distribuição normal de média
uma amostra aleatória de uma distribuição normal de média ![]() e variância conhecida e igual a
e variância conhecida e igual a ![]() .
O objetivo é fazer um gráfico da função de log-verossimilhança.
.
O objetivo é fazer um gráfico da função de log-verossimilhança.
Solução:
Vejamos primeiro os passos da solução analítica:
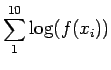 |
|||
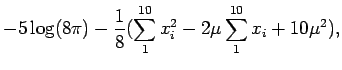 |
(3) |
Vamos ver agora uma primeira possível forma de fazer a função de verossimilhança no R.
> x <- c(12, 15, 9, 10, 17, 12, 11, 18, 15, 13)
> sx2 <- sum(x^2) > sx <- sum(x)
mean(x)) e portanto vamos definir tomar valores ao redor deste ponto.
> mu.vals <- seq(11, 15, l=100)
> lmu <- -5 * log(8*pi) - (sx2 - 2*mu.vals*sx + 10*(mu.vals^2))/8
![[*]](crossref.png)
> plot(mu.vals, lmu, type='l', xlab=expression(mu), ylab=expression(l(mu)))
![\begin{figure}\centerline{\includegraphics[width=0.5\textwidth]{figuras/vero01.ps}}\end{figure}](img251.png) |
Entretanto podemos obter a função de verossimilhança no R de outras forma mais geral e menos trabalhosas.
Sabemos que a função dnorm calcula a densidade ![]() da distribuição normal e
podemos usar este fato para evitar a digitação da expressão acima.
da distribuição normal e
podemos usar este fato para evitar a digitação da expressão acima.
> logvero <- function(mu, dados){
sum(dnorm(dados, mean = mu, sd = 2, log = TRUE))
}
> mu.vals <- seq(11, 15, l=100) > mu.vals > lmu <- sapply(mu.vals, logvero, dados = x) > lmuNote na sintaxe acima que a função
sapply aplica a função logvero anteriormente definida em cada elemento do vetor mu.vals.
> plot(mu.vals, lmu, type='l', xlab=expression(mu), ylab=expression(l(mu)))
Para encerrar este exemplo vamos apresentar uma solução ainda mais genérica que consiste em criar uma função que vamos chamar de vero.norm.v4 para cálculo da verossimilhança de distribuições normais com ![]() =4.
Esta função engloba os comandos acima e pode ser utilizada para obter o gráfico da log-verossimilhança para o parâmetro
=4.
Esta função engloba os comandos acima e pode ser utilizada para obter o gráfico da log-verossimilhança para o parâmetro ![]() para qualquer amostra obtida desta distribuição.
para qualquer amostra obtida desta distribuição.
> vero.normal.v4 <- function(mu, dados){
logvero <- function(mu, dados)
sum(dnorm(dados, mean = mu, sd = 2, log = TRUE))
sapply(mu, logvero, dados = dados)
}
> curve(vero.normal.v4(x, dados = x), 11, 15,
xlab=expression(mu), ylab=expression(l(mu)))
Considere agora a amostra armazenada no vetor y:
> y <- c(5, 0, 3, 2, 1, 2, 1, 1, 2, 1)de uma distribuição de Poisson de parâmetro
lik.pois <- function(lambda, dados){
loglik <- function(l, dados){sum(dpois(dados, lambda = l, log = TRUE))}
sapply(lambda, loglik, dados = dados)
}
E podemos usar esta função para fazer o gráfico da função de verossimilhança como visto à esquerda da
Figura ![[*]](crossref.png)
> lambda.vals <- seq(0, 10, l=101) > loglik <- sapply(lambda.vals, lik.pois, dados=y) > plot(lambda.vals, loglik, ty = "l") ## ou mudando o texto do eixos > plot(lambda.vals, loglik, type = "l", xlab=expression(lambda), > ylab=expression(l(lambda))) ## ou > curve(lik.pois(x, dados=y), 0, 10)
Alternativamente pode-se fazer um gráfico da função deviance, como nos comandos abaixo.
> dev.pois <- function(lambda, dados){
> lambda.est <- mean(dados)
> lik.lambda.est <- lik.pois(lambda.est, dados = dados)
> lik.lambda <- lik.pois(lambda, dados = dados)
> return(-2 * (lik.lambda - lik.lambda.est))
> }
> curve(dev.pois(x, dados=y), 0, 10)
## fazendo novamente em um intervalo menor
> curve(dev.pois(x, dados=y), 0.5, 5)
O estimador de máxima verossimilhança é o valor que maximiza a função de verossimilhança
que é o mesmo que minimiza a função deviance.
Neste caso sabemos que o estimador tem expressão analítica fechada
![]() e portanto calculado com o comando.
e portanto calculado com o comando.
> lambda.est [1] 1.8
Caso o estimador não tenha expressão fechada pode-se usar maximização
(ou minimização) numérica.
Para ilustrar isto vamos encontrar a estimativa do parâmetro da Poisson
e verificar que o valor obtido coincide com o valor dado pela expressão fechada do estimador.
Usamos o função optimise
para encontrar o ponto de mínimo da função deviance.
> optimise(dev.pois, int=c(0, 10), dados=y) $minimum [1] 1.800004 $objective [1] 1.075406e-10
A função optimise() é adequada para minimizações envolvendo um único parâmetro.
Para dois ou mais parâmetros deve-se usar a função optim()
Finalmente os comandos abaixo são usados para obter graficamente o intervalo de confiança baseado na verossimilhança.
corte <- qchisq(0.95, df=1)
abline(h=corte)
## obtendo os limites (aproximados) do IC
l.vals <- seq(0.5,5,l=1001)
dev.l <- dev.pois(l.vals, dados=y)
dif <- abs(dev.l - corte)
ind <- l.vals < lambda.est
ic2.lambda <- c(l.vals[ind][which.min(dif[ind])],
l.vals[!ind][which.min(dif[!ind])])
ic2.lambda
## adicionando ao gráfico
curve(dev.pois(x, dados=y), 1, 3.5,
xlab=expression(lambda), ylab=expression(l(lambda)))
segments(ic2.lambda, 0, ic2.lambda, corte)